El entrenamiento y la selección estratégica de datos en scRNA-seq
El entrenamiento en análisis de datos ómicos como scRNA-seq se enfoca principalmente en herramientas, pipelines y algoritmos. Sin embargo, uno de los factores más determinantes en el aprendizaje es la selección de los datos con los que se entrena.
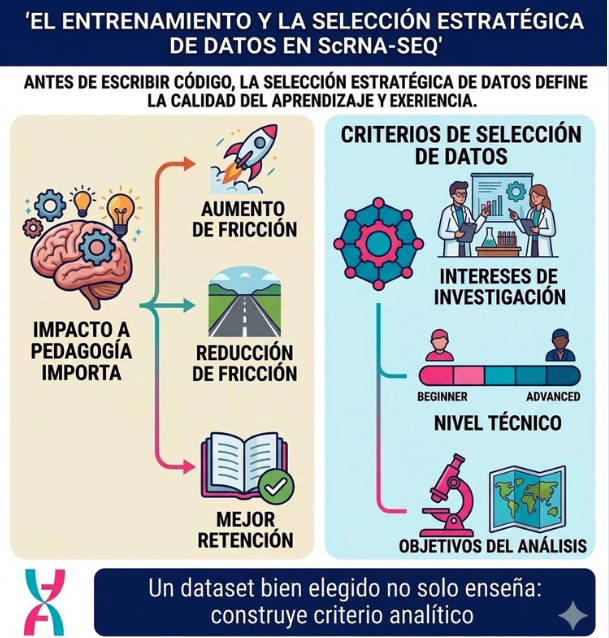
Antes de escribir una sola línea de código, la calidad de la experiencia de aprendizaje ya está siendo definida por el tipo de datos elegidos.
El diseño y la pedagogía importan
El diseño instruccional y la selección adecuada de datos no solo transmiten conocimiento técnico, sino facilitan la inmersión en el proceso de aprendizaje.
Cuando los contenidos, ejercicios y datos están alineados con el contexto del estudiante:
- Se reduce la fricción inicial
- Se incrementa la motivación
- Se favorece la retención
En el aprendizaje de datos ómicos, esto significa que no basta con usar “cualquier conjunto de datos público”. Es necesario elegirlos estratégicamente.
Rol crítico de la selección de datos scRNA-seq en el aprendizaje
Recomendamos utilizar datos específicos alineados, en la medida de lo posible, a:
- Intereses de investigación del grupo
- Nivel técnico de los participantes
- Objetivos del análisis (flujo completo vs flujos específicos avanzados)
“Los datos bien elegidos permiten construir criterio analítico”
Datos curados y reales para aprendizaje
En El Arkhe partimos de una premisa clara: no todos los datos enseñan lo mismo.
El diseño instruccional no solo define qué enseñar, sino también con qué datos se construye el criterio analítico. Elegir datos no es una decisión técnica menor, es una decisión pedagógica central.
Por ello, mantenemos una “curaduría activa de datos”, seleccionados estratégicamente para acompañar la progresión del aprendizaje:
- Desde sistemas altamente estandarizados que facilitan la comprensión inicial
- Hasta contextos biológicos complejos que exigen interpretación, criterio y pensamiento crítico.
Este enfoque permite transitar de ejecutar workflows a entender profundamente los datos y sus implicaciones biológicas.
Más que una comparación técnica, la siguiente tabla funciona para ilustrar una guía pedagógica estudiada para seleccionar datos según el objetivo de aprendizaje:
| Mammalia 10x Genomics | Human Brain Lieber Institute | Arabidopsis plantScGRN |
|---|---|---|
| Marcadores bien definidos | Marcadores menos evidentes | Marcadores limitados y emergentes |
| Tipos celulares del sistema inmune | Tipos celulares específicos de cerebro | Identidades celulares definidas por tejido (root, leaf, vascular) |
| Anotación más sencilla | Análisis más interpretativo | Anotación basada en contexto de desarrollo |
| Células (scRNA-seq) | Núcleos (snRNA-seq) | Principalmente células (protoplasting requerido) |
| Datasets estándar de referencia | Datasets enfocados en investigación | Datasets en rápida evolución con menor estandarización |
| Alta disponibilidad de referencias | Disponibilidad moderada de referencias | Referencias fragmentadas entre estudios |
| Fuerte consenso en la comunidad | Requiere experiencia específica del campo | Requiere conocimiento en biología vegetal |
| Separación clara de tipos celulares | Diferencias transcripcionales sutiles | Transiciones graduales de estado celular (developmental gradients) |
Exploración de curaduría dedatos
Como parte del taller, trabajamos con una curaduría de datos seleccionados estratégicamente para cubrir distintos niveles de aprendizaje:
Datos de 10x Genomics
- Flujos completos desde datos crudos (FASTQ)
- Introducción al pipeline estándar con Cell Ranger
- Base para aprendizaje estructurado y reproducible
Datos del Lieber Institute (human brain)
- Datos enfocados en la habenula humana
- Conexión directa con investigación real
- Ejemplo de análisis en sistemas biológicos complejos
Datos de planta Arabidopsis
- Alternativa para contextos agrícolas y biología vegetal
- Enfoque en desarrollo, diferenciación y regulación génica
- Ideal para transicionar hacia análisis interpretativo
La colección completa de datasets y recursos está disponible para los participantes del taller o bajo solicitud directa.
Experiencia de aprendizaje efectiva
El flujo de trabajo enfocado en incorporar datos alineados a los intereses del grupo de participantes, así como ajustes pertinentes a su nivel técnico, permite:
- Comprensión conceptual sólida
- Práctica técnica contextualizada
- Mayor autonomía en análisis
Y, sobre todo, una inmersión de aprendizaje más enriquecedora que promueve el aprendizaje continuo.
Reflexión final
En scRNA-seq, aprender no es solo ejecutar pipelines.
Es interpretar datos, formular preguntas y generar conocimiento.
Y ese proceso comienza con la elección correcta de los datos y un diagnóstico preciso del nivel del participante. Aspecto fundamental de nuestro diseño pedagógico en los talleres de El Arkhe MultiOmics.
¿Te interesa este enfoque?
¿Te gustaría colaborar, aportar datos o conocer más sobre nuestra propuesta formativa?
📩 Escríbenos a elarkhe@gmail.com
Explora nuestros talleres de análisis de datos ómicos: Índice de talleres
Ver la curaduría de datos: Explorar datos
¿Te interesa la próxima edición del taller de scRNA-seq?
Registrate para recibir más información sobre la próxima edición del taller, incluyendo fechas, temario y detalles de inscripción.
Referencias y recursos
-
Transcriptomic Analysis of the Human Habenula in Schizophrenia
American Journal of Psychiatry
https://psychiatryonline.org/doi/10.1176/appi.ajp.20240776 -
Supporting open-access version (PMC)
https://pmc.ncbi.nlm.nih.gov/articles/PMC11119547/ -
10x Genomics Datasets Repository
https://www.10xgenomics.com/datasets
Cynthia S Cardinault (2026). El entrenamiento y la selección estratégica de datos en scRNA-seq. En Talleres MultiOmics. El Arkhe.